当质控报告不合格时,我们就需要对reads进行修剪,修剪的工具有很多,今天简单介绍一下trim galore。
下图是fastqc生成的html文件

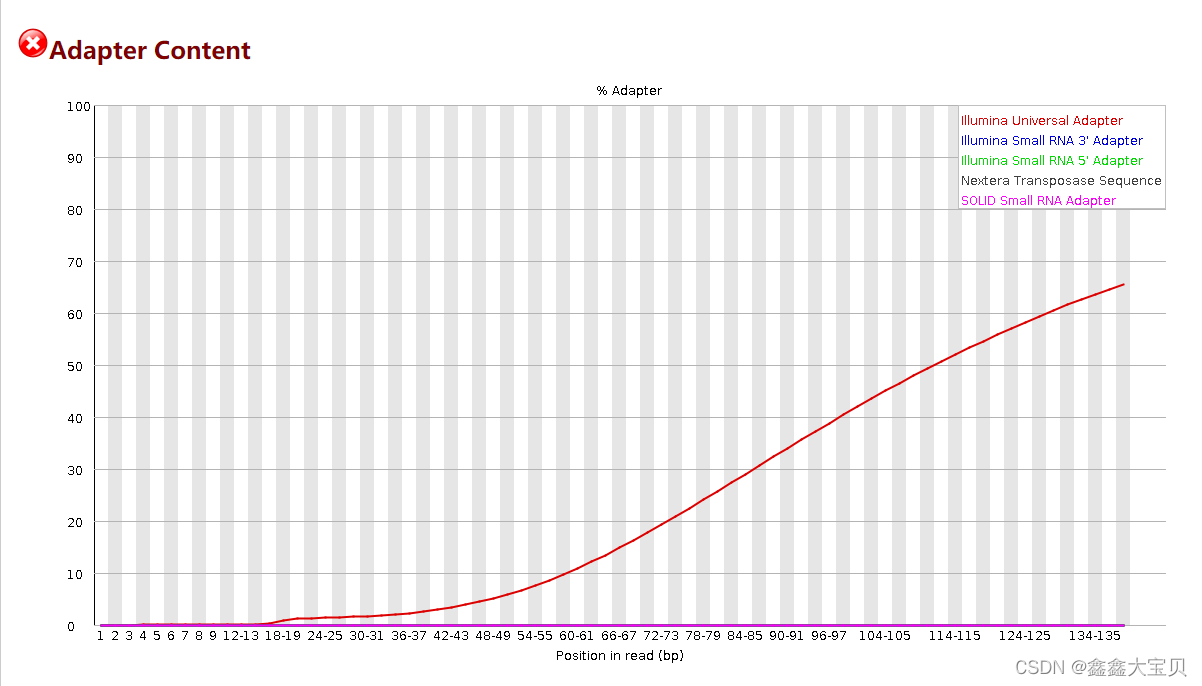
可以看到per base sequence content是错误的,并且Adapter Content也是错误的,说明需要对reads进行修剪处理。
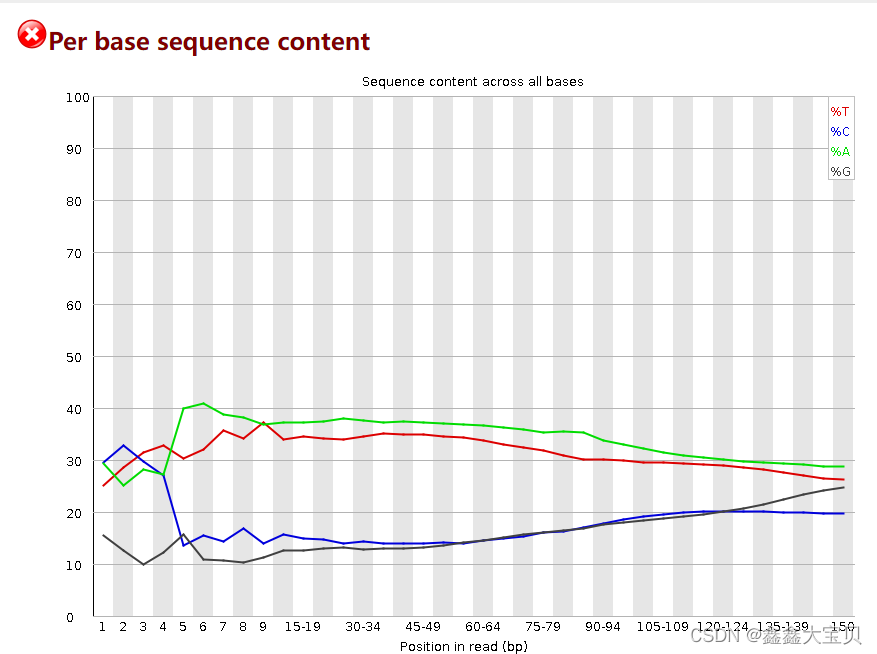
理论上来说,A和T应该相等,C和G应该相等,且相互平行,但一开始不稳定,所以会出现一开始的情况。所以需要对该条reads进行修剪。
trim_galore --phred33 --paired --fastqc --clip_R1 5 --three_prime_clip_R1 15 --clip_R2 5 --three_prime_clip_R2 15 输入fastqc文件一 输入fastqc文件二 -o 输出文件路径
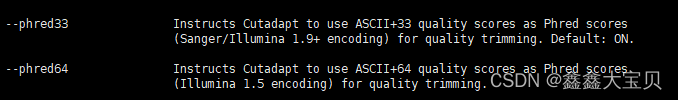
输入trim_galore -help就可以看到trim_galore所有的参数了,下面只截取了上述代码包含的参数
![]()
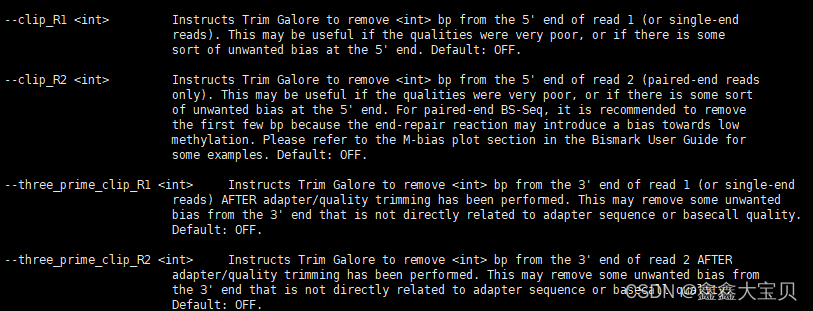
从html文件中的per base sequence content中可以看到,前面15个bp需要被修剪掉,后面5个bp需要被修剪掉(不用太严格,删减太多也不好)。所以设置参数为
--clip_R1 5 --three_prime_clip_R1 15 --clip_R2 5 --three_prime_clip_R2 15
同学们可以自己查查各参数代表什么意思。运行代码后,将会产生新的html文件,我们打开进行对比。

可以看到两个需要改善的地方都合格了,先来看看per base sequence content
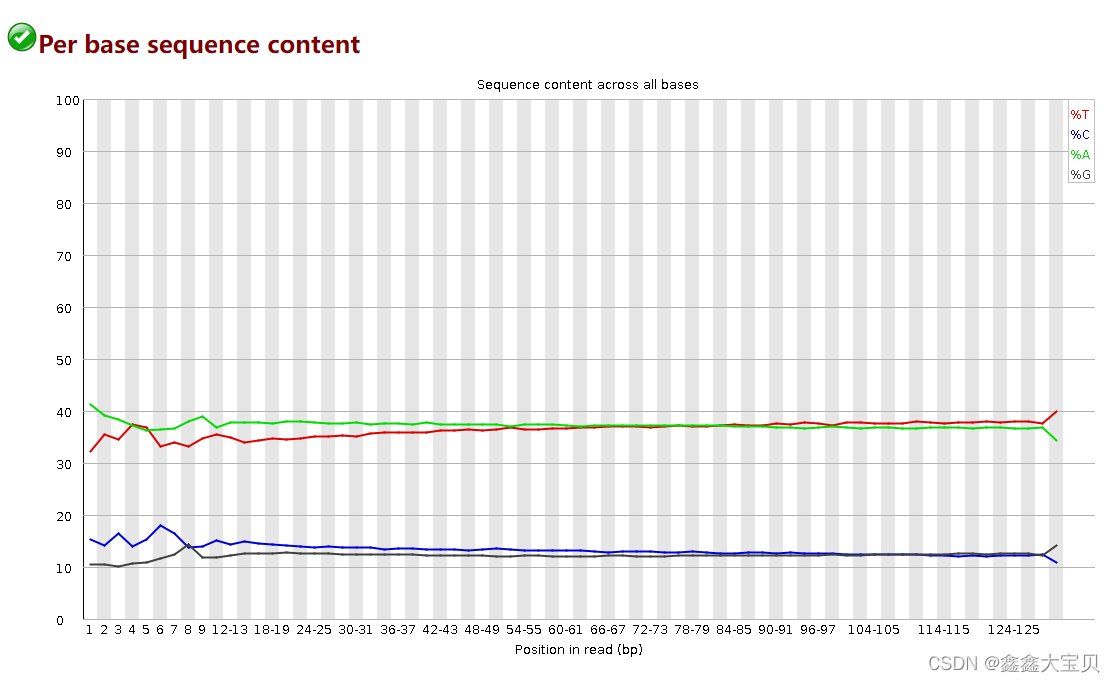
可以明显观察到比之前好多了,前端还是有一些不正常但也无妨。
同时我们发现Adapter Content也显示正常了,这是因为trim galore会自动去除Adapter。
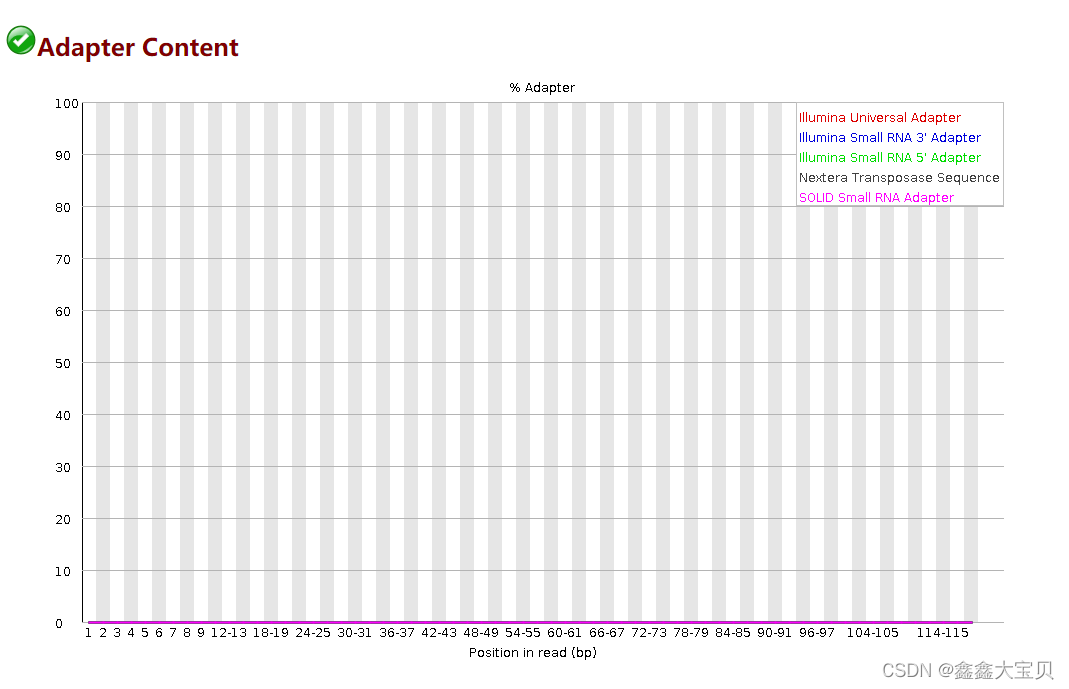
感谢观看!