TCGA数据库甲基化数据的下载
1、登陆TCGA官网
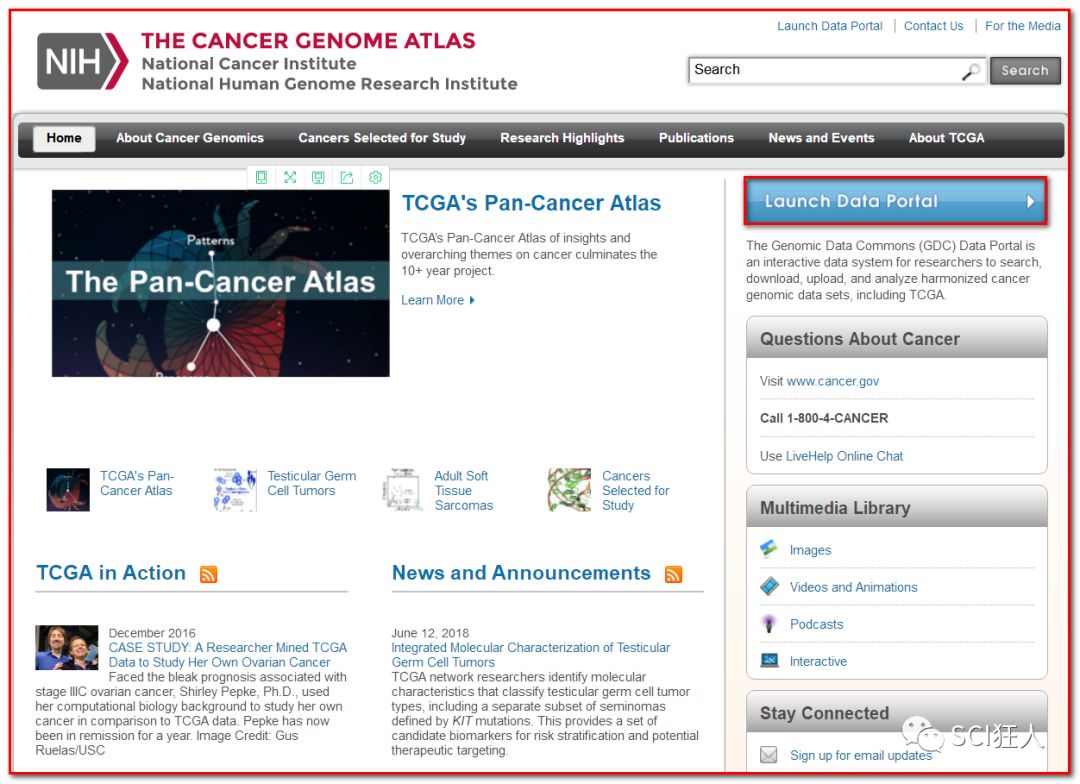
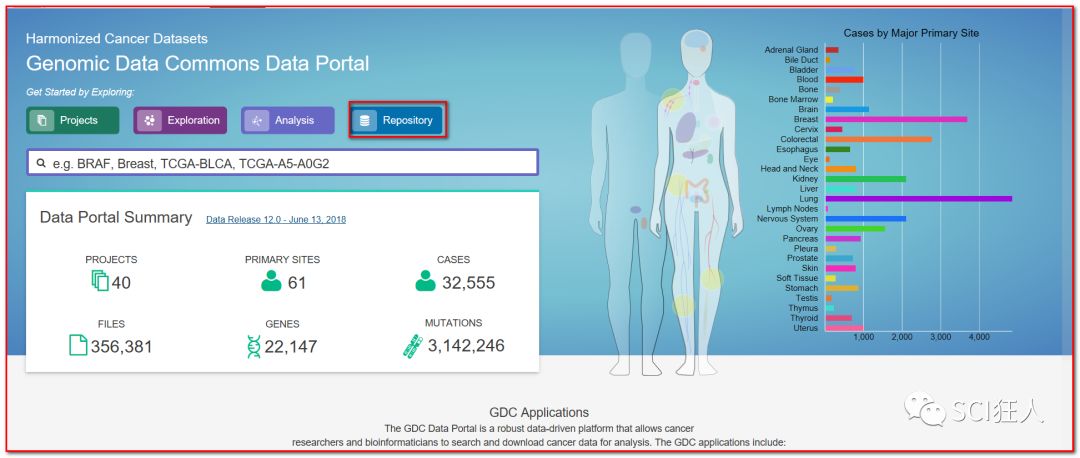
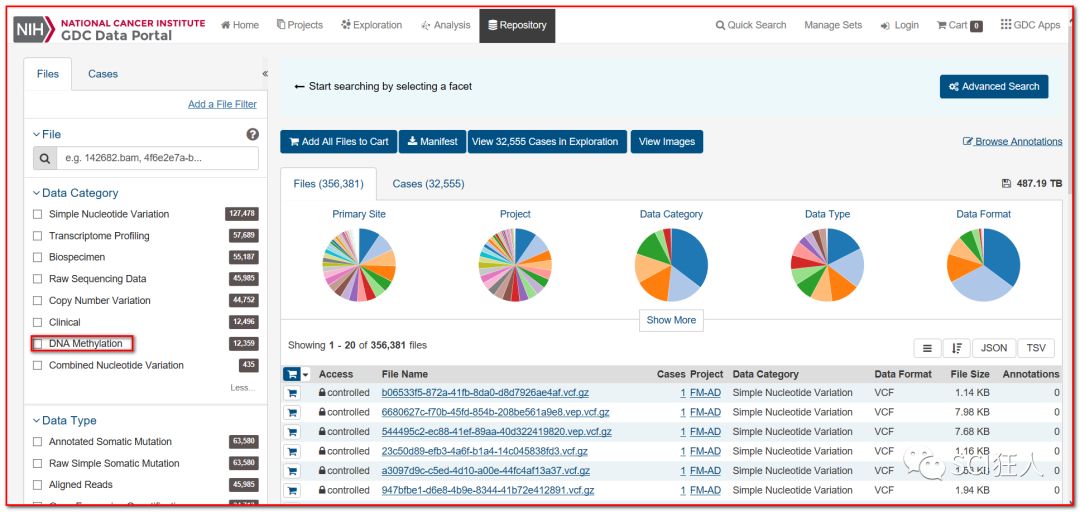
2、选择下载DNA Methylation
3、选择癌症
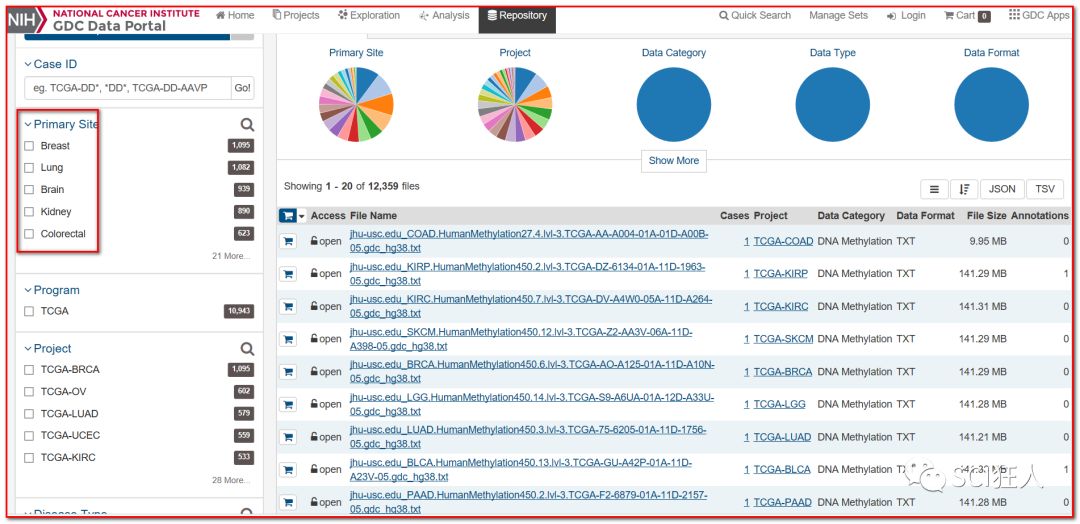
4、添加到cart
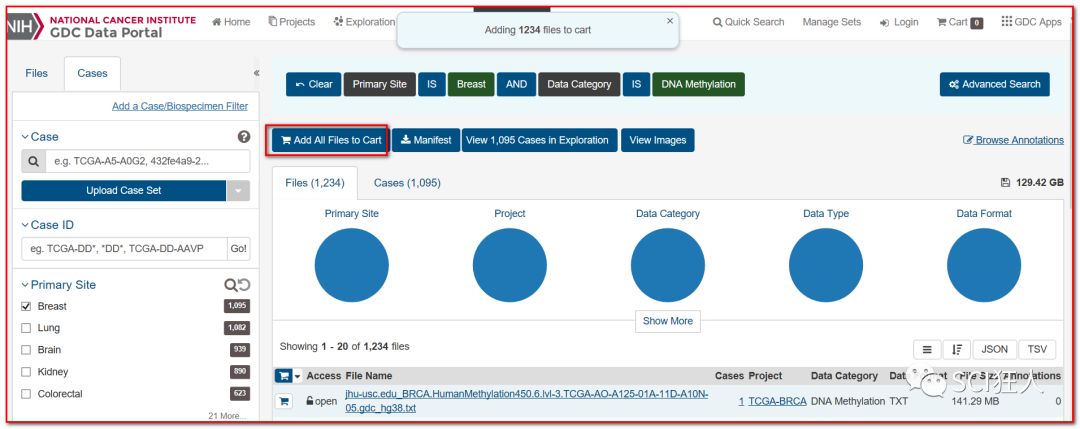
5、点开cart就可以下载了
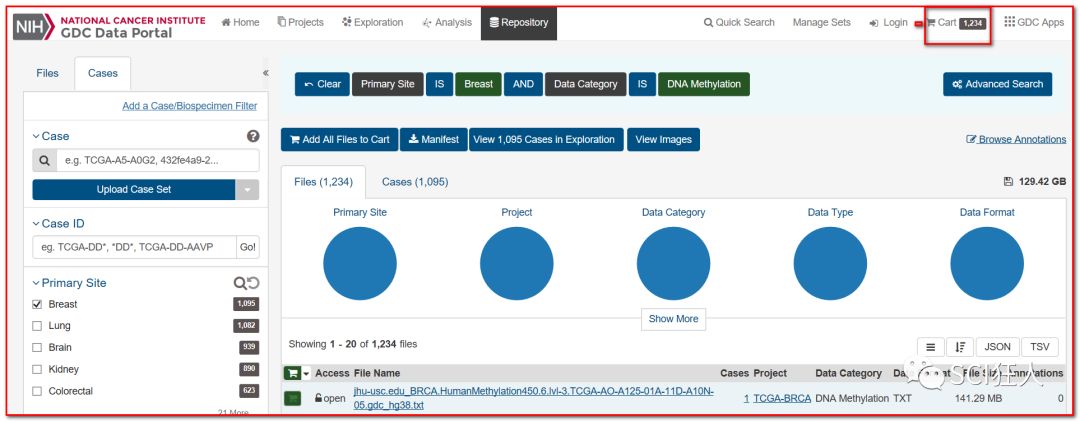
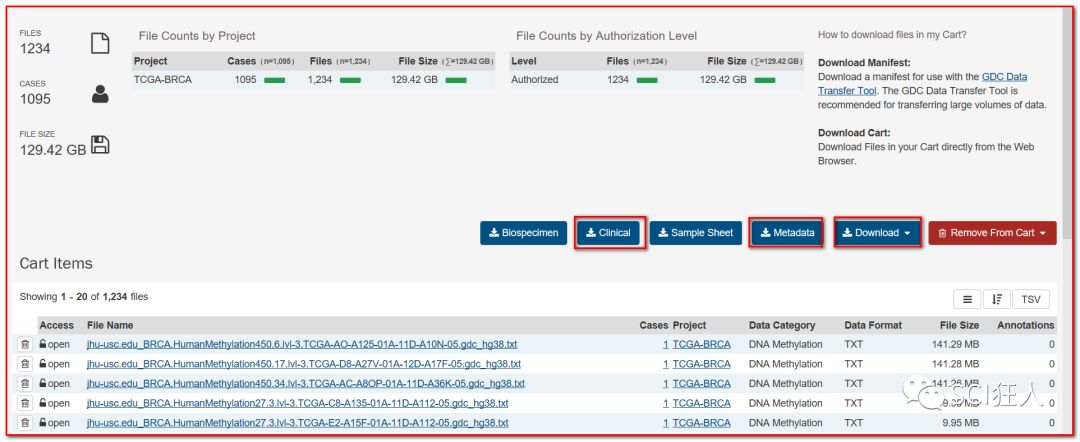
然后把得到cart文件和gdc-manifest文件放在同一个文件夹,然后按住shif键同时点击鼠标右键,点击“在此处打开命令窗口(shell)”如下图:
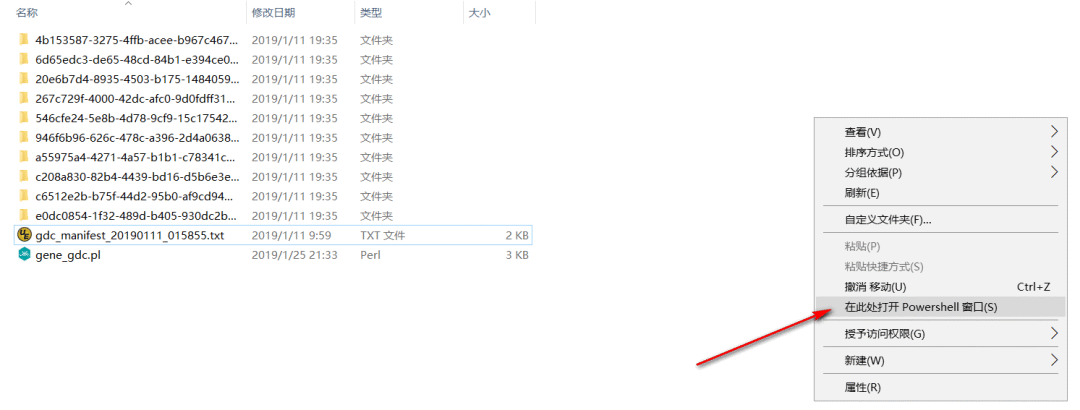
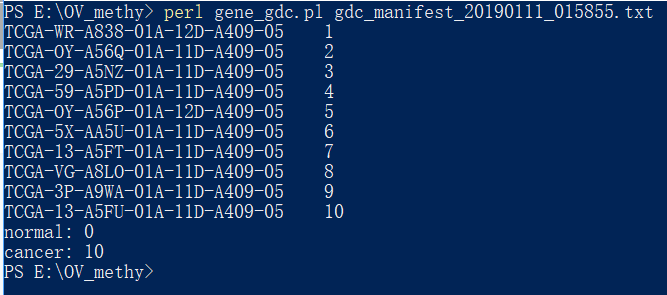
然后输入脚本(电脑要安装perl)命令;
perl gene_gdc.pl gdc_manifest_20190111_015855.txt(改为自己的manifest文件名), 然后按回车即可
待光标返回原来的目录即可得到结果
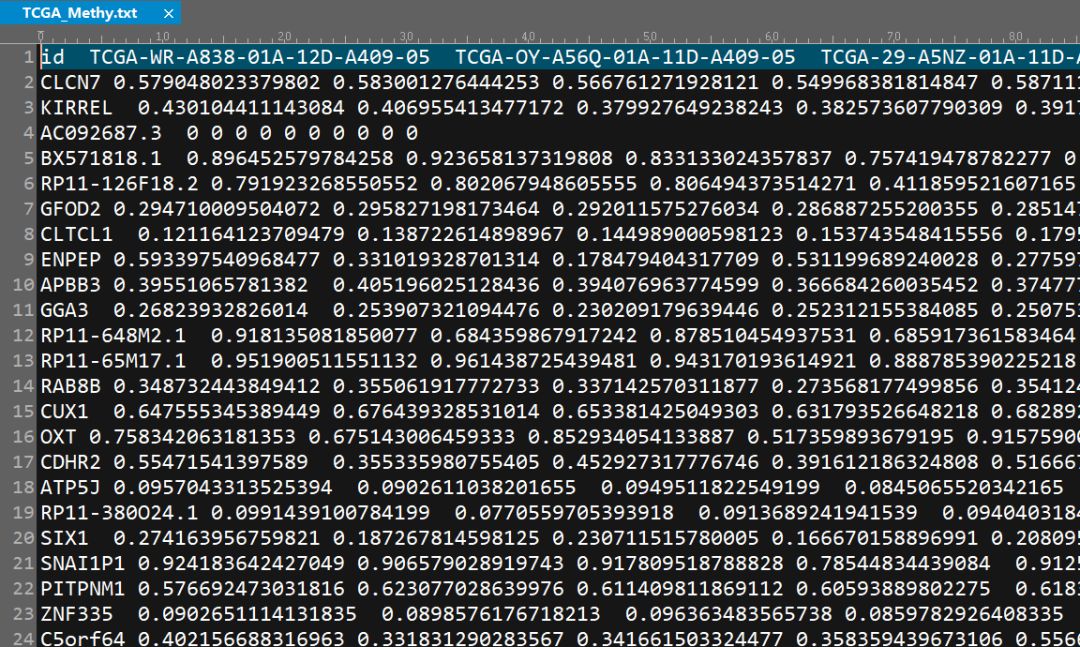
然后就可以得到基因在各个位点平均甲基化程度,然后可以分析了
上面的脚本是非卖品,购买SCI狂人团队VIP会员的朋友可以免费赠送~SCI狂人团队VIP会员。TCGA甲基数据是非常的,一般都是几十个G,对电脑配置要求非常高,即使有了脚本也很难提取出来,除非你的电脑够强悍。当然,也可以找我们帮忙下载和提取的,每种癌症的价格是500元(每人只限一种),VIP会员可以免费获取2这种癌症数据,这样你就不需要担心数据下载不了,数据提取不出来,或者下载数据和提取数据需要几个星期。
猜你喜欢的文章►这就是你需要发SCI的套路
►SCI狂人团队VIP会员
►TARGET之ceRNA(首发,抢发)
►聪明的人都在用这个数据库构建ceRNA
►这样的论文小学生应该也可以
►全亚洲发文最快的套路
►这种套路你肯定可以
►SCI=简单数据挖掘+简单实验
►不做meta分析,不做生信数据挖掘,利用这个数据库就可以发一大堆SCI
►miRNA既然可以这样挖掘
►这种套路既可以发文章,也可以作为课题设计
►TCGA miRNA数据挖掘文章分享
►TCGA lncRNA挖掘学习文献
►抢发,抢发!
►纯数据挖掘的ceRNA貌似快成为下一个meta了
►有钱也不一定能够发高分文章
►批量挖掘TCGA lncRNA的机会来了
►批量挖掘TCGA临床数据的机会来了
►没有数据发文章?不存在的
►这批数据等着你去挖掘
►GEO数据挖掘的深度不够,有没有提高GEO数据挖掘的深度的方法呢?
►国自然标书里面最好不要列出这些期刊的文章
►想不到课题?不存在的
►生信数据挖掘选刊,就这服两个期刊
►干湿结合发文套路
►做数据挖掘的你需要这款牛逼软件
► 免费课程再次上线
►批量挖掘TCGA lncRNA的机会来了
►批量构建TCGA lncRNA Cox回归模型?
►SEER数据挖掘这样玩才过瘾的
► 遇到这样的导师已经很不错了
► 批量挖掘TCGA让发文速度更加快
► GO富集分析这种图,你也可以呀
► 这也许是全亚洲发SCI最快的方法
► 环状RNA在非肿瘤方向的研究
► 贝叶斯网状meta分析应该怎么样学呢?
► 非肿瘤方向应该怎么样做预测模型?
► 想不到课题?不存在的
► GEO数据挖掘的深度不够,有没有提高GEO数据挖掘的深度的方法呢?
► TCGA这样挖掘才爽的
► GEO lncRNA 数据挖掘的文献分享
► 国自然经费预算需要注意这些
► 这样的基础科研套路你也可以
► 如何快速学习GEO数据挖掘?
► Meta分析这么烂了,还能玩吗?
